研究内容CONCEPT
研究概要
生体分子はタンパク質やDNAの立体構造のようにその要素の組み合わせで自由に構造や空間を作成することが可能です。本グループでは、これらの生体分子を用いたデザイン可能な構造や空間(バイオアーキテクチャ)と化学を融合することで、ナノサイエンス、イメージング・センシング、材料応用や生体応用へとつながる新たな分子テクノロジーを創出することを目指しています。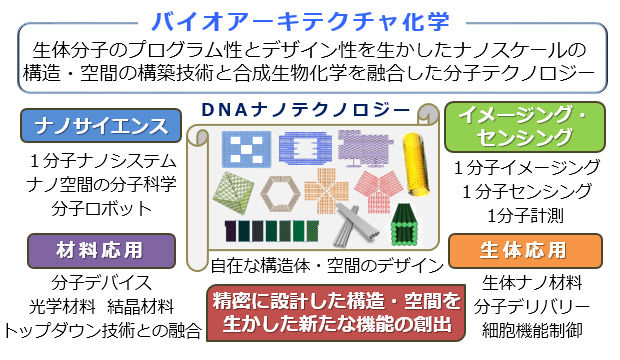
私たちのグループでは、さまざまな平面構造と立体構造のデザインと作成を行えるDNAオリガミ技術を用いて、DNA配列の設計を行い、ナノ構造体やナノ空間の構築を行うことで、 (1) 新規な2次元及び3次元ナノ構造体の構築とその操作、(2) 2次元DNA構造体の配列プログラムに従った精密な配列と機能化、(3) DNAナノ空間内での生体分子反応の制御と操作、(4) DNAナノ空間での1分子の挙動や反応の可視化と解析、(5) DNAナノ空間での生体分子の物性の解明、(6) 新規DNA結晶の開発、(7)1分子で動作する分子デバイスの開発、(8) 光学材料への応用、(9) 分子ロボットへの応用、(10) 細胞へのデリバリーシステムの開発、(11) 診断・治療への応用を研究しています。 本グループでは、目的に応じたDNAナノ構造体の設計・構築、ナノスケールで新規機能を発揮する分子デバイス・分子システムの開発、生体機能解明のための1分子イメージング・分析システムの開発、新規バイオナノマテリアルによる生体への応用を目指しています。これらの研究のため、私たちのグループでは、実時間測定可能な高速原子間力顕微鏡(AFM)を備えています。
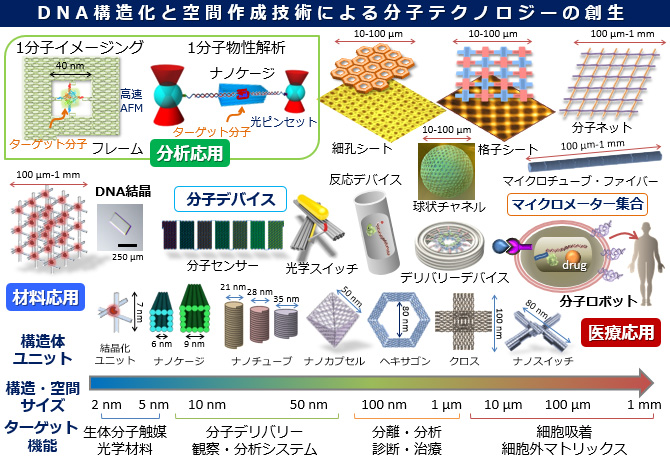
DNAオリガミ構造と空間作成技術を使った分子テクノロジーの概要:(A)様々な形状とサイズ (nm~mm)のDNAオリガミ構造体・空間・集合体の設計と開発. (B) 新規分子ナノシステムの開発.(C)空間を利用した分析システムの開発.(D)新規分子デバイスと機能性材料への応用.(E)細胞機能の制御と診断医療への応用.
3次元DNAナノ構造の構築と機能化
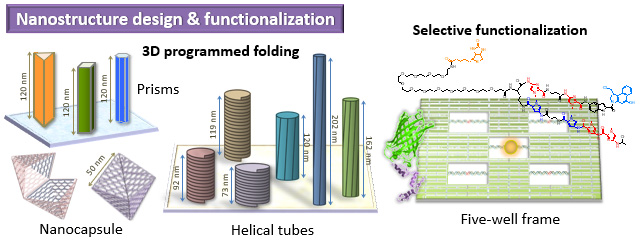
DNAオリガミ技術を用いてさまざまな平面構造や立体構造を設計し作成しています。作成したDNAオリガミ構造体には様々な機能の付加を行います。そのために位置特異的に分子を固定する技術の開発を行っています。
ナノスケールでのプログラム配列化と制御
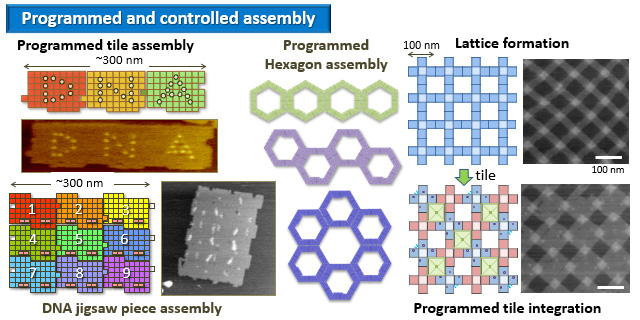
あらかじめプログラムした通りにDNAオリガミ構造体を配列できるシステムの開発を行っています。外部刺激に応じてDNAオリガミ構造体の集合や解離をコントロールできるシステムも開発しています。
生体分子の動きと反応の1分子イメージング
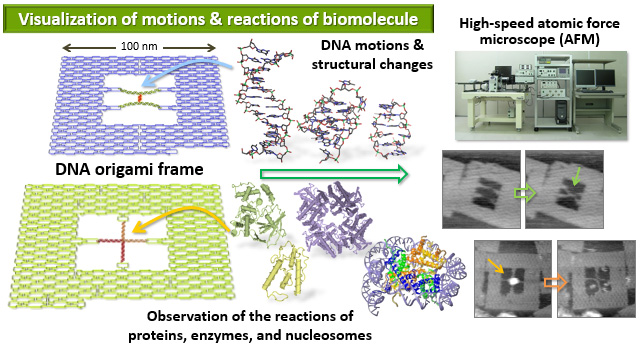
DNAオリガミ構造体にターゲットとなるDNA鎖を固定し、酵素反応やDNAの構造変化の1分子観察を行っています。分子の動きを実時間で捉えられる高速原子間力顕微鏡(AFM)を使用し、イメージングを行っています
ナノスケールの分子集積システムの開発
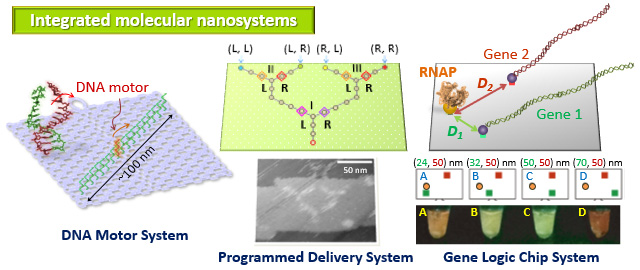
特定の分子に応答して機能発現する分子システムの開発を行っています。DNAオリガミ構造体に分子を精密に配列・集積し、分子モーターの動きや転写を制御しています。
メカニカル分子デバイスの開発
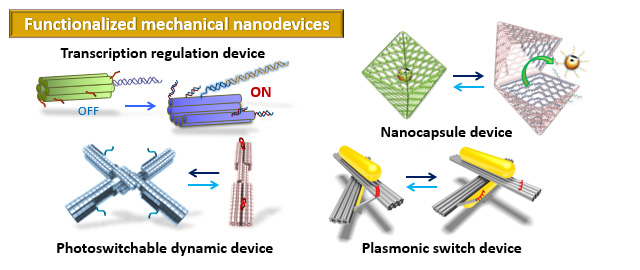
機械的な動作を行う分子デバイスの開発を行っています。生体分子や光によって駆動し、DNAオリガミ構造体の構造変化などの動作によって機能を発現します。光学デバイスや分子デリバリーに使用できます。
1分子センシングシステムの開発
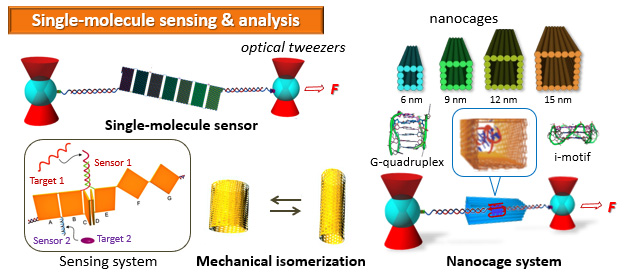
DNAオリガミ構造体と光ピンセットを使った生体分子の1分子分析システムを開発を行っています。生体内を模倣してDNA構造体で作成した狭小空間での生体分子の物性の研究も行っています。
細胞操作と生体への応用
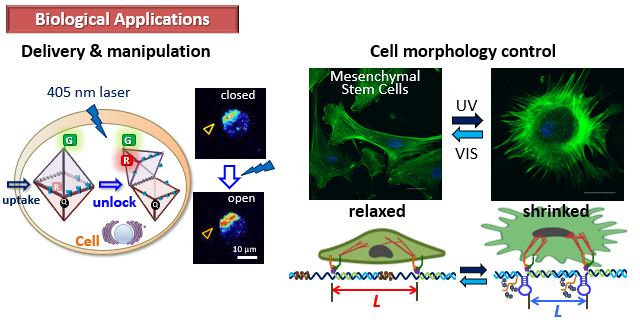
光に応答するカプセル状のDNA構造体を使った細胞への輸送システムと細胞内での選択的な光操作を行っています。また、光に応答するDNAナノマテリアルによって幹細胞の形態変化の操作を行っています。
現在の主な研究テーマ
1. 新規な多次元DNAナノ構造の設計と構築と機能化
2. DNAナノ構造体のプログラム多次元配列化
3. DNAナノ空間を使用した化学反応や生化学反応の制御
4. 生体機能の解明のための1分子イメージング
5. DNAナノ空間での生体分子の物性の解明
6. 新規なDNA結晶の開発と物性の解明
7. 1分子で機能する多様な分子デバイスの開発
8. 光学特性を持つナノデバイスの開発
9. 分子機械と分子ロボットへの応用
10. 細胞機能を制御する分子システムの開発
11. 診断・治療など生体への応用
光スイッチング可能な機械的DNAポリマーを使った細胞形態の操作
Angew. Chem Int. Ed. in press (2021)
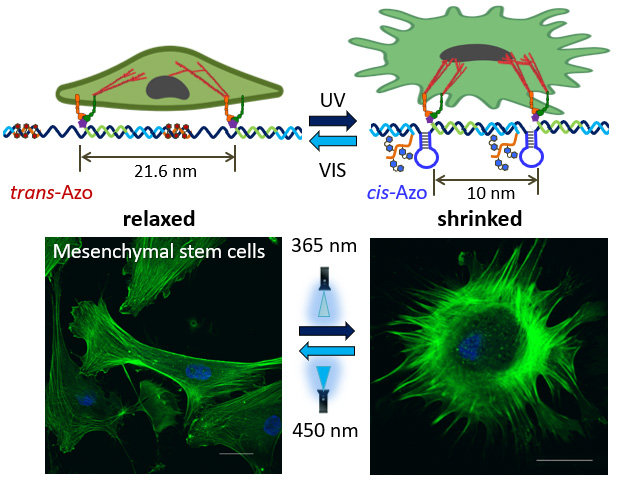
生体に存在する細胞外マトリックスは、細胞に動的で可逆的な環境与えます。特に細胞が形態形成、修復、および分化を受けている際に、空間的および時間的な操作は細胞にとって不可欠です。ナノスケールの操作を可逆的にできるこれらの複雑なシステムは、重要な細胞プロセスをよりよく理解するのに役立ち、in
vitroで細胞機能を正確に操作することを可能にします。ここでは、アゾベンゼンを含む光スイッチ可能な動的なDNAナノ構造を構築し、光照射による光スイッチ可能なDNAポリマーを使用して、接着ペプチド間の空間距離を動的に操作しました。AFMによる観察で、光応答性DNAポリマーはリラックスした直線構造と収縮したコンパクトな構造を可逆的に形成することがわかりました。このDNAポリマーの機械的特性を使用して、UVおよび可視光の照射により、間葉系幹細胞(MSC)の形態が丸い形状と紡錘状の形状に大きく変化し、細胞内の関連遺伝子の発現の変化も見られました。この光応答性システムは、細胞外マトリックスの形態との相関をみるためのツールとなります。この研究は、幹細胞と刺激応答性の機械的DNAナノ構造体の間のナノスケールの相互作用を探索するための方法論を提供します。
DNAオリガミ構造体を利用した光制御可能なCRISPR-Cas9システムの構築
CHemm. Commun. 57, 5594-5596 (2021)
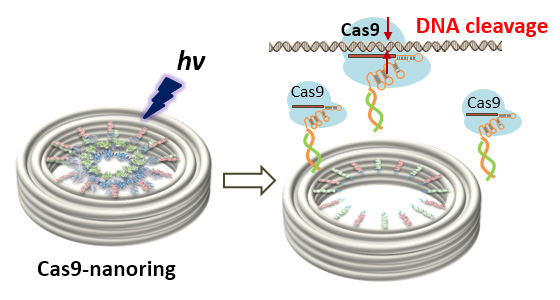
ガイドRNA(sgRNA)によって配列を選択できるCRISPR-Cas9システムは配列選択的なゲノム編集の強力なツールとして注目を集めています。 このCRISPR-Cas9システムとDNAナノ構造体を利用して配列選択的なDNA切断を光反応により制御しました。ここでは、DNAオリガミナノリング構造体にsgRNAを介してCas9を導入し、光切断部位組み込むことで光制御されたCas9によるDNA切断を検討しました。 ナノリング内に組み込まれたCas9は切断活性を示さないのに対して、光照射によってCas9がナノリングから放出さることで、放出されたCas9は選択的なDNA切断の活性を示しました。 DNAオリガミナノ構造体の空間にCas9を閉じ込めることで酵素活性を抑制でき、光照射による酵素の放出により再活性できることを示しました。 このシステムは、細胞内の遺伝子発現制御などに利用できます。
原子間力顕微鏡を用いたDNA結晶表面のナノスケール観察と結晶の形成と分解の動的な観察
Chem. Commun. 57, 1651-1654 (2021)
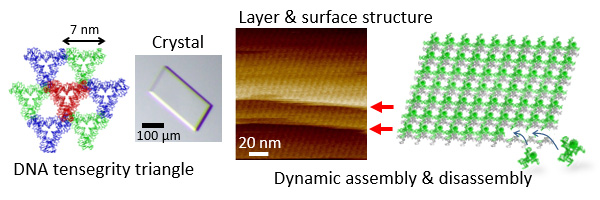
自己集合性のDNA結晶は、DNA配列を変えることで結晶の格子を設計でき、分子を結合することで機能化できるため、注目されています。 Seemanのグループによって作成されたDNAテンセグリティトライアングル構造は、DNA結晶化に使用された最初のビルディングブロックで、多くの機能化が行われてきました。 本研究では、結晶表面を分子スケールで観察することにより、結晶成長のメカニズムの理解を目指しました。 本研究では、原子間力顕微鏡(AFM)を使用して、テンセグリティトライアングルのDNA結晶の形成と分解を直接観察しました。 AFMで結晶表面を観察し、組み立てられた三角形ユニットの格子配位を分子レベルで特性評価しました。 DNA結晶とモノマーユニットの集合をナノスケールの解像度で特性評価し、結晶の形成と分解のダイナミクスを結晶層レベルで視覚化しました。 観察バッファー中のモノマーユニットの濃度を調整することで結晶形成と分解を制御できることは明らかになりましたが、形成速度とモノマー濃度の関係はまだ分かっていません。 この方法は、未知の結晶の特性評価とその形成プロセスに利用できます。
2種類の光スイッチを使用したDNAオリガミの集合と解離の光制御
Chem. Eur. J. 27, 778−784 (2021)
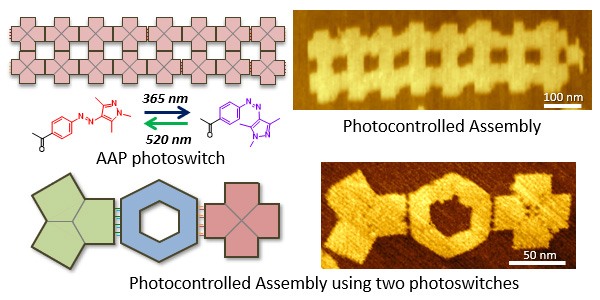
刺激応答性スイッチング分子は、生体分子の機械的制御を目的として広く研究されています。最近開発されたアリールアゾピラゾール(AAP)は、従来使用されているアゾベンゼンと比較して、光異性化に対する応答が速く、独自の吸収スペクトル特性を持っています。ここでは、光によるDNAオリガミナノ構造体の集合と解離を制御するため、AAPが光スイッチング分子として使用できることを検討しました。 AAPを導入したDNAオリガミを設計・構築しました。 AAP修飾X型DNAオリガミ(X)と相補鎖を持つ六角形オリガミ(H)の可逆的な集合と解離は、UVと可視光照射を交互に行うことで達成しました。 AAP修飾X型オリガミの四量体と直線状のアセンブリは、光照射によって正確に形成され、1 μmを超える線形アセンブリが形成されました。最後に、2個の光スイッチ、AAPとアゾベンゼンをそれぞれDNAオリガミに導入し、異なる照射波長を使用することにより、異なる集合体の形成を制御できることを明らかにしました。 AAPを光スイッチに使用することで、利用できる波長を拡張し、さまざまなDNAオリガミナノ構造体の集合と解離を安定に行うことができます。
配置と方向を制御したヌクレオソーム間の動的な相互作用の直接観察
Chem. Eur. J. 26, 15282−15289 (2020)
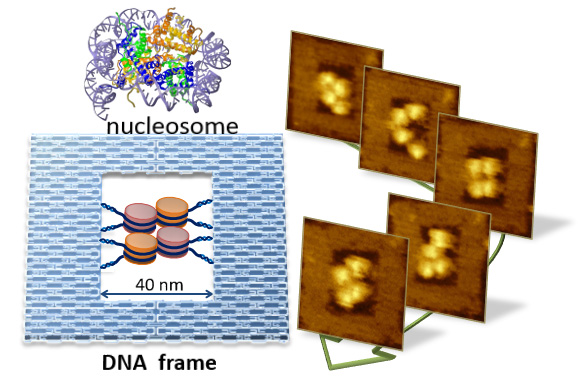
ヌクレオソームは、遺伝子発現とそれに続く細胞の発生、分化、及び細胞機能の発現に関与する最も基本的な複合体です。 ここでは、高速原子間力顕微鏡を使用して直接観察するために、再構成したヌクレオソームをDNAオリガミフレームに配置する方法を開発しました。この方法を使用すると、複数のヌクレオソームをDNAフレームに組み込むことができ、ヌクレオソームのリアルタイムの動きを可視化できます。 ヌクレオソームの配置とコンフォメーション、2個のヌクレオソーム間の距離を設計して制御し、 さらに、4個のヌクレオソームをDNAフレームに配置しました。 それぞれのコンフォメーションで複数のヌクレオソームは十分接近でき、これらの間に相互作用が見られました。また、個々のヌクレオソームの動的な動きは、DNAフレーム内で正確に追跡でき、それらの位置関係と相互作用を直接観察できました。この手法を使うことで、一般的に必要なマイカの表面修飾もヌクレオソームの化学的固定も不要で、DNAフレームはヌクレオソームを保持するだけでなく、それらの自然な状態も保持します。 この方法は、ヌクレオソームの相互作用を検討でき、クロマチン構造を研究するための有望なプラットフォームを提供します。
逆方向結合した環状PIP-DNA複合体のX線結晶構造解析
J. Am. Chem. Soc. 142, 10544−10549 (2020)
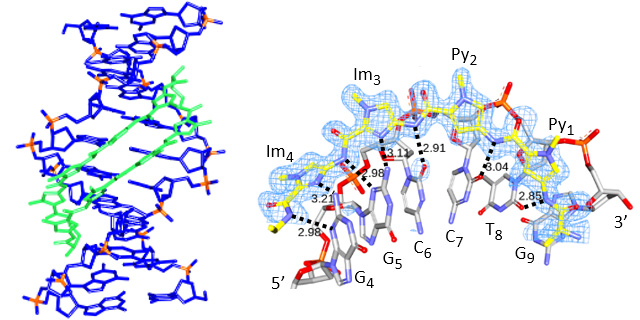
二本鎖DNAと結合分子間の相互作用の解明は遺伝子調節に使用されるDNA結合分子の設計に重要な情報を与えます。ピロールイミダゾールポリアミド(PIP)は、二本鎖DNAの配列特異性を持つ合成DNA結合分子です。ここでは、DNAと複合化したキラル環状PIP(cPIP)のX線結晶構造を1.5Åの解像度で解析し、cPIPがDNA副溝の逆方向に結合することを明らかにしました。結晶構造から、cPIPの塩基とピロールイミダゾール部分の間の水素結合の位置が、順方向と逆方向の両方で類似し、cPIPの結合によって引き起こされるB型DNA構造の歪みが明らかになりました。さらに、cPIP分子の両端にあるγターンユニットのアミノ基とDNAの間に新しい水素結合が形成されることを見出しました。リバースPIPの向きをフォワードPIPと比較することで、この研究で使用したS体のcPIPのリバース方向での選択的な結合は、cPIP-DNA複合体の全体的なコンフォメーション、特に水素結合の配置に由来することがわかりました。これらの結果から、副溝でのcPIP結合の異なる立体選択的な結合について明らかになりました。
ナノスケール空間中での2本鎖DNAの物性
J. Am. Chem. Soc. 142, 10042−10049 (2020)
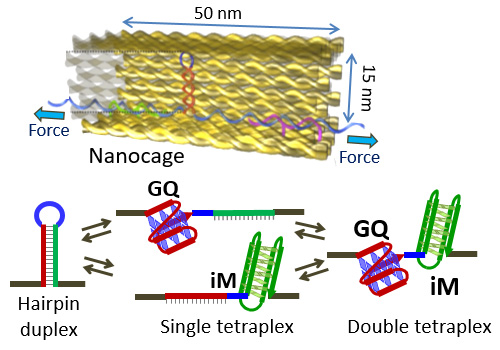
グアニン四重鎖やiモチーフなどの四重鎖DNA構造は、ナノ空間に閉じ込められることで折り畳みが容易になり安定化します。一方で、B型の二重鎖DNAのナノ空間内での特性は解明されていません。ここでは、ヘアピンステムの形で17塩基対のDNA二重鎖を用いて、DNAオリガミで作成したナノ空間内のヘアピン二重鎖DNAの折り畳みとアンフォールドの特性を光ピンセットによる1分子力計測で検討しました。この結果、溶液中と比較して、15×15 nmサイズの空間中で、ヘアピンDNAの機械的安定性(20→9 pN)及び熱力学的安定性(25→6 kcal/mol)は大きく減少しました。自由エネルギープロファイルから、ヘアピンDNA二重鎖のアンフォールドの活性化エネルギーが大幅に減少(28→8 kcal / mol)することが分かり、遷移状態の構造は折り畳まれていない状態に近いことがわかりました。このことは、ヘアピン二重鎖DNAがナノ空間に閉じ込められることで、その安定性が弱められることを示しています。相補的なテロメアのグアニン四重鎖(GQ)/i-モチーフ(iM)形成配列を含むヘアピンDNAでは、GQまたはiMに使われるHoogsteen塩基対の形成が、Watson-Crick塩基対よりも好ましいことがわかりました。これらの結果は、ナノチャネル、ナノポア、ナノポケットのようなナノ空間内でのDNAの挙動にも当てはまると考えられます。また、ナノ空間が多く存在する細胞内環境で、B型DNAよりも非標準的なDNA構造が優先される別の経路の存在が解明されると考えられます。
DNAオリガミ構造体による抗菌分子のデリバリーシステム
Angew. Chem. Int. Ed. 59, 12698–12702 (2020)
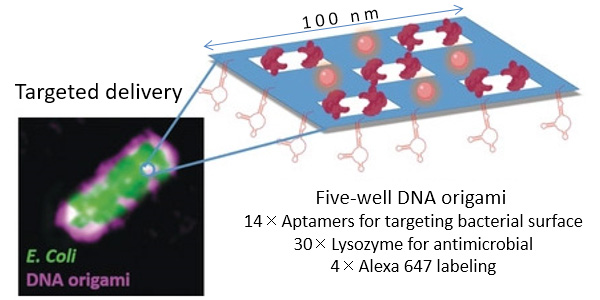
抗生物質耐性は、世界的に拡大している問題であり、代替となる抗菌戦略が早急に必要とされています。本研究では、特定の効率的な方法で抗菌酵素リゾチームを送達するための手段として、アプタマーで機能化したDNAオリガミナノ構造体を開発しました。リゾチームと蛍光ラベルを導入し作成した分子システムをグラム陽性(Bacillus subtilis)とグラム陰性(Escherichia coli)のターゲットに対して検討しました。超解像顕微鏡(d STORM)と原子間力顕微鏡(AFM)を使用して機能化したDNAオリガミ構造体を同定し、構造化照明顕微鏡(SIM)によって、機能化したDNAオリガミとバクテリアの結合を見ました。その結果、リゾチーム機能化DNAオリガミによって処理すると、リゾチーム単独による処理よりも効果的にバクテリアの増殖を遅らせることが明らかとなりました。これらの結果から、抗生物質耐性克服のツールとして機能性DNAオリガミが有効であり、ドラッグデリバリー手段としてDNAオリガミ構造体の特異性とその効率が実証されました。
DNAオリガミナノチップ上でのTET酵素を介した酸化反応の制御
Nucleic Acids Res. 48, 4041–4051 (2020)
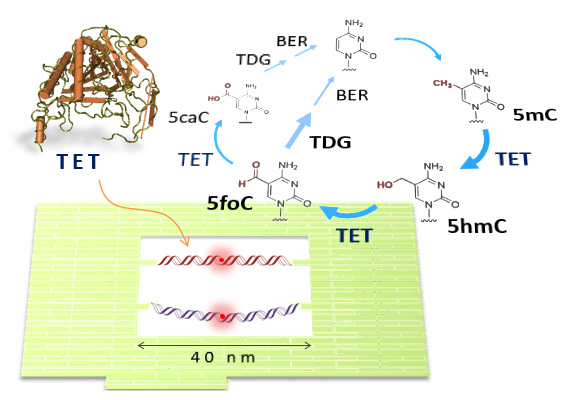
TETタンパク質は、CpG部位での5-メチルシトシン(5mC)を連続的に酸化し、エピジェネティックな遺伝子発現制御で中心的な役割を果たします。本研究では、DNAオリガミナノチップで5mCのTETを介した酸化を制御し、原子間力顕微鏡(AFM)によりDNAナノチップでの単一分子TETタンパク質の挙動を観察しました。 5mCを含む基質二本鎖DNA(dsDNA)2本を導入したDNAオリガミフレームを使用しました。まず、DNAナノチップ内でdsDNAを張り詰めた状態とリラックスした状態に制御して、TETによる酸化とTDGによる塩基除去への影響を調べました。酵素結合とDNAナノチップでの酸化反応の検出から、TETは、5-メチル化シトシンの酸化修飾の種類に関係なく、リラックスした基質で反応しやすいことが分かりました。次に、複数の5mCGサイトを持つ基質を使用し、TETがヘミメチル化サイトよりもフルメチル化サイトを好むことを見出しました。また、高速AFM(HS-AFM)によるTETの動的な動きを観察し、スライディングやストランド間ジャンプなどの物理的なプロセスを直接観察しました。さらに、DNAナノチップでTDGの5foC塩基除去を観察しました。このように、私たちのシステムは、酵素反応を物理的に制御でき、ナノスケールレベルでのDNA脱メチル化プロセスの観察と特性評価に使用できます。
光応答性転写因子GAL4のダイナミクスの直接観察と解析
Angew. Chem. Int. Ed. 58, 7626-7630 (2019)
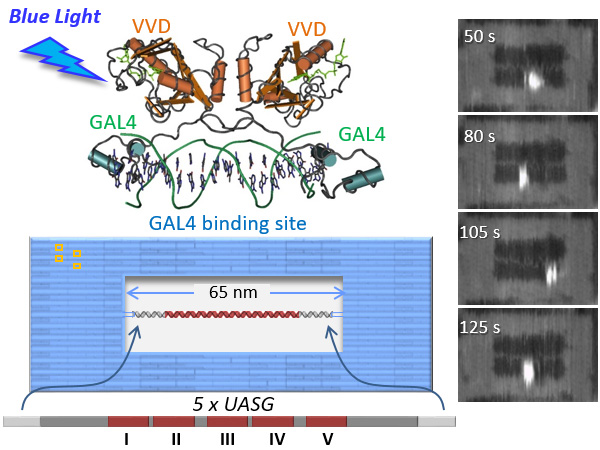
光応答性転写因子GAL4(GAL4-VVD)の動的な挙動をDNAオリガミ構造の空間を使い直接観察を行いました。 高速AFMを用いて、GAL4-VVDと基質DNAの光に応答した複合体形成を観察しました。GAL4結合配列を含む2本の基質DNA鎖を用いて、結合、スライディング、停止、解離など、GAL4-VVDの動的挙動が観察されました。 また、2本の二本鎖DNA間で鎖間ホッピングを観察しました。 さらに、5個の結合部位を含む長い基質DNA鎖を用いると、結合、スライディング、停止、解離を含む一連のGAL4-VVDとDNAとの相互作用が観察されました。詳細な分析によって、GAL4-VVDは、特異的結合部位を迅速に探索するためにスライドおよびホッピングを使用して二本鎖DNA上をランダムに移動し、その後安定な複合体形成のために特異的な配列に結合することが明らかになりました。 このことは、GAL4のスライディングと認識に対する異なる結合様式の存在を示唆しています。ナノスケールの解像度でこの一分子イメージングシステムは、DNA結合タンパク質の探索のメカニズムに対する様々な知見を与えてくれます。
光ケージしたナノカプセルの細胞内での解錠と開口の制御
Bioconjugate Chem. 30, 1860-1863 (2019)
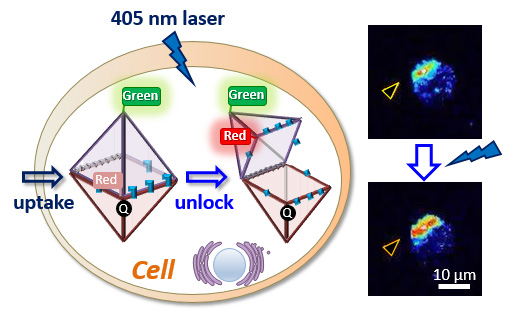
細胞への分子デリバリーのキャリアの作成を行うため、光によってロックを解除できるシステムを備えたメカニカルなナノサイズのDNAカプセルを設計・構築しました。
光照射によるカプセルの開口を制御するため、光ケージシステムをナノカプセルに導入しました。 原子間力顕微鏡(AFM)によってナノカプセルの開口を観察し、また、蛍光消光からの回復によってナノカプセルの動的な開口を検討しました。
光ケージしたナノカプセルを細胞に導入、細胞質に局在させ、その後に光照射によってカプセルの開口を蛍光イメージングで観察しました。個々の細胞へのレーザー照射によって細胞中での光ケージしたナノカプセルの選択的な解錠と開口に成功しました。
UPF1によるステムループRNAの翻訳依存性の巻き戻しとそれに伴うRegnase-1による炎症性mRNAの分解
Nucleic Acids Res. 47, 8838–8859 (2019)
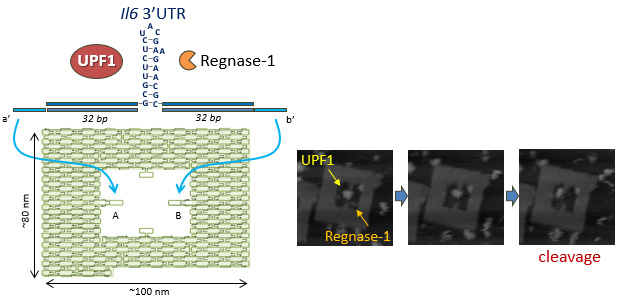
特定のステム・ループ構造を持つ炎症性mRNAのRegnase-1を介した分解は、適切な免疫恒常性を保つのに重要な役割を担います。最初の翻訳の前に、Regnase-1はターゲットのステム・ループと結合しますが、ヌクレアーゼによる切断を行いません。AFMによる1分子イメージングによって、UPF1が最初にステム・ループを巻き戻すために必要であり、RNAの分解を進めるためにRegnase-1を結合することを明らかにしました。翻訳後、Regnase-1は2つの異なる位置で、UPF1と結合します。Regnase-1のRNaseドメインは、UPF1のSMG1リン酸化残基T28に結合します。加えて、Regnase-1の不規則なセグメントはUPF1のRecAドメインに結合し、UPF1のヘリカーゼ活性を増強します。
SMG – UPF1 – Regnase-1複合体は、初期の翻訳過程をターゲットとして、特定のmRNAによって翻訳されるタンパクの数を制限することによって炎症を迅速に解消します。さらに、SMG1の小分子による阻害は、樹状細胞でのRNAの巻き戻しを防ぎ、自然免疫応答の転写後の制御を可能とします。
金属イオンを介した塩基対形成と二本鎖DNA形成のナノスケール空間を使った直接観察
Chem. Eur. J. 25, 1446-1450 (2019)
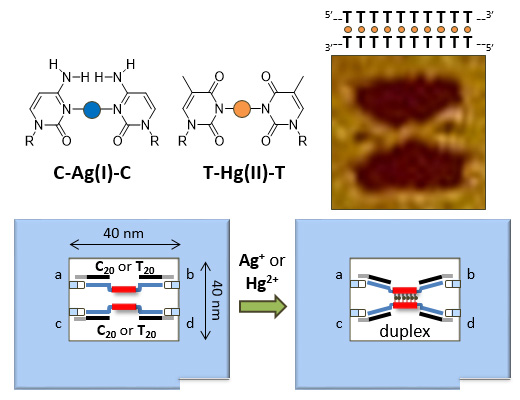
設計したナノスケール空間を使って、金属イオンによって誘導される二本鎖DNAの形成をAFMによる1分子イメージングで検討しました。金属イオンを介した塩基対形成を、C-Ag-CおよびT-Hg-T金属塩基対を使って検討しました。 連続したCまたはTを含むターゲットDNA鎖をDNAフレームに組み込み、その結合を金属イオンの添加により制御しました。 組み込まれたDNA鎖の構造変化をAFM観察し、二本鎖DNAの形成が確認されました。 さらに、T-Hg-T塩基対を用いて、二本鎖DNAの動的な形成とその解離を観察しました。さらに、DNAナノ構造空間を使って、連続したT-Hg-T塩基対の持つ特徴的な形状の二本鎖DNAの視覚化に成功しました。
ナノケージ中の水の活量の評価とG-quadruplexとi-motifのフォールディングへの影響
Proc. Natl. Acad. Sci. USA, 115, 9539-9544 (2018)
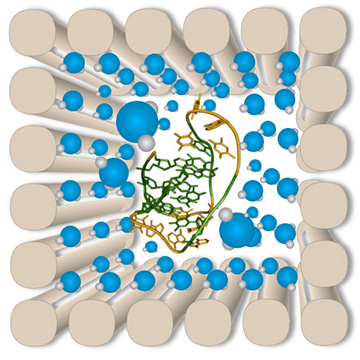
ナノスケール空間内で分子は特異な性質を示しますが、空間内部に含まれる水の性質を調べるのは非常に困難です。 本研究では、G-quadruplexおよびiモチーフ構造の折りたたみの際に放出される水分子の量を測定し、9
X 9nmから15 X 15 nmの空間を持つDNAナノケージ中の水の活量を見積もりました。この結果、ケージサイズを小さくすると水の活量が減少することが分かりました。
9×9 nmのケージでは、ポリエチレングリコール(PEG)のような通常の共溶媒の到達範囲を超えて水の活量が低下しました。 この一連のナノケージを用いて、G-quadruplexまたはiモチーフの折りたたみの過程全体で水分子の変化を見ることができました。
これらのことから、水分子の全体的な損失によって、水の活量が低下したナノケージ中のG-quadruplexまたはiモチーフの折りたたみが促進されることが分かりました。
DNAオリガミ上に統合した遺伝子ロジックチップ
Nature Nanotechnology,13, 933-940 (2018)
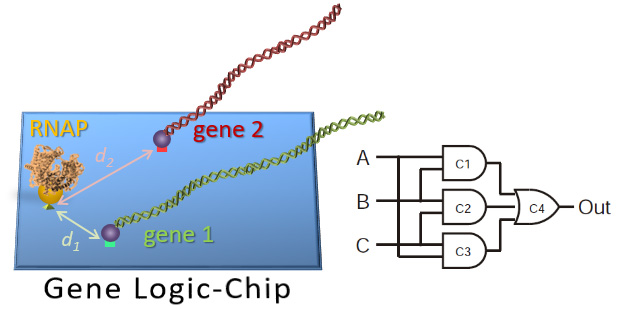
合成生物学において、遺伝子発現の制御は、生物学的シグナルの多段階計算を必要とします。しかしながら、遺伝子回路間のクロストークを完全に回避することは困難であるため、複雑な遺伝子回路を作成することは困難でした。本研究では、DNAオリガミ上に、T7
RNAポリメラーゼ、と複数の基質となるターゲット遺伝子を乗せたナノチップにアクチュエータとセンサーを導入して、直交型の内蔵型デバイスを作成しました。この遺伝子ナノチップは、それぞれの遺伝子を直交的に転写し、DNAオリガミの分子をレイアウトする能力をつかって酵素と基質遺伝子間の距離を制御することにより遺伝子発現レベルを合理的に設計でき、距離に依存した遺伝子発現に成功しました。さらに、マイクロRNAのプロファイルを計算できるリプログラミング可能な論理ゲートを統合して、ナノチップが遺伝子ロジックチップとして機能することを証明しました。私たちのナノチップ上のコンポーネントを統合するアプローチは、大規模な統合された遺伝子回路の作成の基盤になると考えています。
形状の相補性を使ったDNAオリガミフレームワークへのDNA構造体の精密な配列化
Angew. Chem. Int. Ed. 57, 7061-7065 (2018)
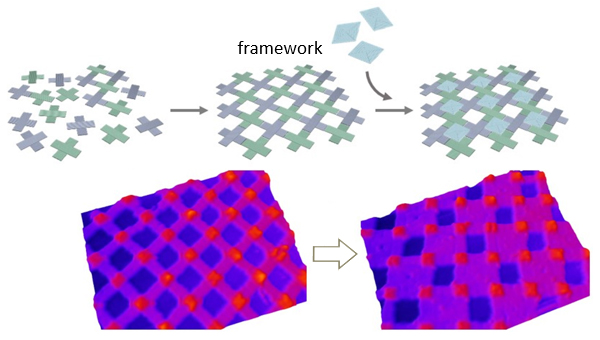
自己集合したDNAオリガミアレイは明確で周期的な空間を持ち、様々なナノスケールの構造体を組み込むことができます。ここでは、あらかじめ組み立てた2次元DNAオリガミフレームワークの内部空間を使用して、空間の形状にフィットした正方形のDNAオリガミ(SQ)を組み込みました。このアプローチでは、格子状のフレームワークは、十字形DNA
オリガミからマイカ上に形成させた脂質二重層膜上で自己集合させ、続いてSQ を添加しました。高速AFMを用いて、SQ-オリガミが動的に吸着・脱離する挙動を観察でき、フレーム内で連続的にその位置が動いていくことが観察されました。SQ-オリガミはMg2+濃度を増加させることによって、またはSQ-および十字型オリガミの両方に相補的なDNA鎖を導入することによって、フレーム内に正しく配置させることができました。このシステムの特徴を使い、2つの異なる十字型オリガミユニットから集合させたフレームワークを用いることによって、SQ-オリガミを市松模様のパターンに配置することに成功しました。この得られた研究成果は、複数のDNAオリガミからなる超分子構造・システムを作成するためのプラットフォームとして使用できます。
DNAオリガミを足場に使った四量体Kir3カリウムイオンチャネルの集積化と機能
Angew. Chem. Int. Ed. 57, 2586-2591 (2018)
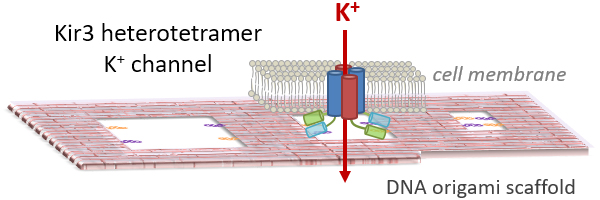
生体中では、シグナル伝達を誘導するために、タンパクを複合体に集合させる際、足場となるタンパクが重要な役割を果たします。こうした考え方は、機能性の膜貫通タンパク複合体を集合させる人工的なシステムには、まだ取り入れられていません。 これを実現するために、DNAオリガミは、特定の位置にタンパクを配置するための理想的な足場として使用することができます。 本研究では、亜鉛フィンガータンパク(ZFP)を介して、Kir3カリウムイオンチャネルタンパクをDNAオリガミ上の特定の位置に集合させることを検討しました。 DNAオリガミへのZFPの結合したKir3チャネル、およびZFPを結合した分子の特異的結合を、AFMとゲル電気泳動分析によって確かめました。さらに、細胞内にDNAオリガミを導入することで、 ZFP結合部位を有するDNAオリガミは、DNAオリガミを導入しない細胞と比較して、ヘテロ四量体Kir3チャネルのカリウムイオンのチャネル電流をほぼ3倍に増加させることを見出しました。 DNAオリガミを足場にするこの方法は、膜タンパク質のオリゴマー化状態を人工的に制御するため有用であることが分かりました。
RecAによる相同配列探索の配向と幾何学的構造の1分子直接観察
ACS Nano, 12, 272-278 (2018)
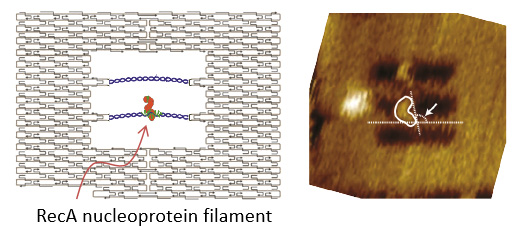
ゲノムの完全性は、発生したDNA損傷によって損なわれた場合、相同組換えによる効率的な修復によって維持されます。このプロセスのために、ユビキタスなリコンビナーゼA(RecA)とその類縁体、例えばヒトRad51は、欠損領域を交換するために、一本鎖および二本鎖DNA内の相同配列を整列させ交換するための重要な役割を持ちます。ここでは、高速AFMを用いて、ターゲットDNAとDNAオリガミフレームと組み合わせ、RecA相同性探索のメカニズムを1分子レベルでAFMによって直接観察しました。この結果、RecA核タンパク質フィラメントが、短距離での拡散、長距離のランダム移動、またはホッピングを含むスライディングを介してDNA鎖に沿って移動することが分かりました。また重要なことに、特異的な相互作用の幾何学的な構造から、相同性を検索する間に、基質二本鎖DNAが、RecA核タンパク質フィラメントのらせんの溝内にある第二のDNA結合部位に存在することを見出しました。この研究は、高速AFMと目的に合ったDNAオリガミを用いることによって、従来の1分子レベルでの観察では不可能であったダイナミックなタンパク-DNA相互作用について、立体配向と幾何学的な情報を直接明らかにできることを実証しました。
DNAオリガミナノ構造体の光制御による動的なコンフォメーション変化の1分子観察
Angew. Chem. Int. Ed. 56, 15324-15328 (2017)
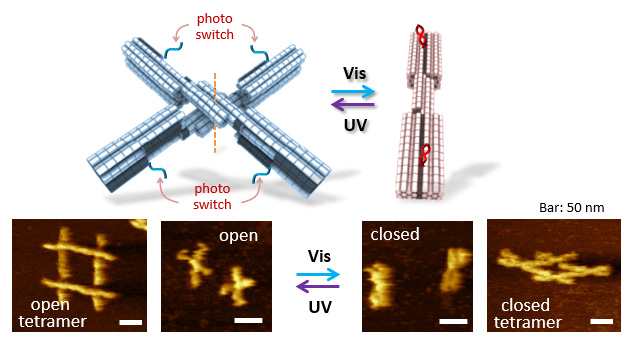
ナノテクノロジーの目標大きな目標には分子ロボット、ナノデバイス、ナノマシンの構築があります。こうした分子機械を作成する際、刺激に応答する分子アクチュエーターが必要になります。本研究では、高速AFMを用いて、光制御可能なDNAオリガミ構造体の動的な開閉の挙動を直接観察しました。まず、塩濃度の変化によって制御される開閉状態の構造変化を、AFM走査中に直接観察しました。次に光応答性部分をナノ構造体に組み込み、光照射によりこれらの構造変化を制御しました。光スイッチ可能なDNA鎖を使用して、光応答性ナノ構造体を作製し、ゲル電気泳動およびAFMイメージングによって、紫外光および可視光の照射後の開閉の立体構造を判別しました。さらに、光照射中のこれらの可逆的な形状の変化を、高速AFMを用いて直接可視化しました。また、UVおよび可視光照射によって開閉制御できるハサミ型のアクチュエータの集合体を4つの光スイッチング可能なナノ構造体から作成し、光操作に成功しました。
サイズが制限された空間でのグアニン四重鎖の折り畳み特性の変化
Nature Nanotechnology, 12, 582–588 (2017)
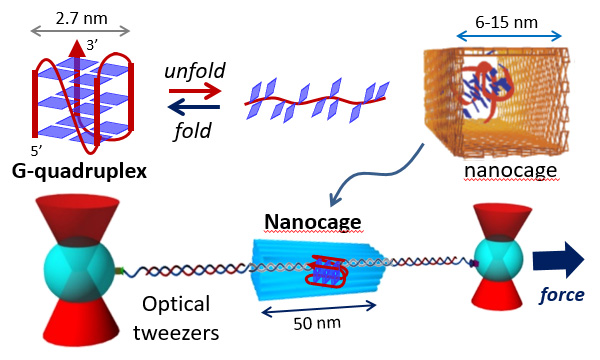
サイズが制限された空間ではエントロピー効果のため、折り畳まれた生体分子構造の安定性を増加させることが分子シミュレーションで示唆されています。制限された空間と閉じ込められた分子構造との間に生じる相互作用があるわけですが、それを明確に実証するための方法がありませんでした。本研究では、DNAオリガミによって作成した分子かご構造体(ナノケージ)を利用して、制限された空間でのヒトテロメアのグアニン四重鎖の形成に対する効果を検討しました。実験では、ナノケージをそのままの構造に保ちながら、グアニン四重鎖の機械的なアンフォールディングを調べました。この結果、ナノケージ内部でのグアニン四重鎖の機械的及び熱力学的安定性は、ケージのサイズの減少にしたがって大幅に増加することがわかりました。安定性の増加は、分子クラウディングした溶液中よりも顕著に現われました。サイズが制限された空間でのグアニン四重鎖のフォールディングの速度は、分子クラウディング状態に比べて100倍高速であり、このことは、DNAまたはRNAポリメラーゼ内部でのグアニン四重鎖が複製あるいは転写で共同的なフォールディングを行う可能性を示唆しています。
Holliday junction分解酵素の葉緑体核様体分離の仲介
Science, 356, 631-634 (2017)

相同組換えの間に形成される4本鎖DNA構造Holliday junctionは、その分解酵素(resolvase)によって解かれます。この酵素は原核生物や真核生物では見出されていますが、植物細胞の小器官では見出されてません。葉緑体の核様体(DNA-タンパク質複合体)の分離ができない緑藻Chlamydomonas reinhardtii変異体を解析することにより、葉緑体中のHolliday junction分解酵素として単核細胞葉緑体1(MOC1)を同定しました。 MOC1は、細菌のHolliday junction分解酵素に構造的に類似し、紫外線(Ruv)Cに対する耐性を持ち、緑色植物間で遺伝的に保存されています。 シロイヌナズナでのMOC1の発現の減少あるいは不発現は、成長の障害および異常な葉緑体の核様体分離を引き起こします。生化学的な分析と高速AFMによる分析により、A. thaliana MOC1(AtMOC1)はHolliday junctionのコアに対称的に結合し切断しました。 MOC1は、Holliday junctionを分解することによって、緑色植物での葉緑体の核様体分離を仲介することが示唆されました。
基質DNA鎖の回転拘束によるCas9切断の影響と反応の1分子観察
J. Am. Chem. Soc. 138, 13842-13845 (2016)
ゲノム編集に用いられるCas9の切断の際に基質DNAの拘束による効果を調べるため、DNA frameを使って拘束した基質DNAを作成しました。DNA frameに結合する様式で回転を拘束したものと回転可能なもの2本鎖DNAを構築しました。Cas9の切断反応はqPCRによって定量し、さらにDNA鎖に結合したCas9が観測され、複合体が基質DNA鎖から解離する様子を高速AFMによって観測しました。これらの結果から、ターゲット鎖ではないDNA鎖が拘束されるとCas9の切断効率が大幅に落ち、ターゲット鎖が拘束されても切断には影響が少ないことがわかりました。このことから、拘束があるDNA鎖はCas9の反応の障壁となることを示唆し、1分子レベルでのCas9の解離の機構に対する知見も得られました。
光による回転制御可能な分子ナノマシーンと回転運動の1分子観察
Chem. Eur. J. 23, 3979-3985 (2017)
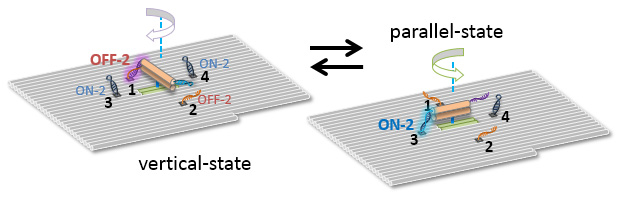
光を入力することによってその回転を調節できる、DNAナノマシンをDNAナノ構造体上に構築しました。ダブルクロスオーバーのDNA回転子は、剛直な分子ワイヤーによってDNAタイルの上に結合しました。2種類の異なる光応答DNAのペアを使うことで、回転子は垂直と平行の二つの状態をとるように回転を調整することができます。また、回転子のリアルタイムの回転運動を、高速原子間力顕微鏡により直接可視化しました。DNAを使って作成したこのナノデバイスは新たなナノスケールの回転装置のプロトタイプとなります。
トポロジーを制御したDNAナノ空間での3重鎖DNA形成の1分子観察可能な分子ナノマシーンと回転運動の1分子観察
Chem. Eur. J. 22, 5494-5498 (2016)
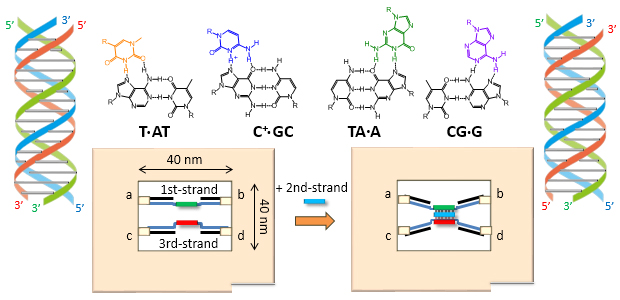
三重らせん形成の1分子イメージングをDNAオリガミ構造体を用いて行いました。 DNAフレーム内の二本鎖DNAへの第三のDNA鎖の結合は、二種類の異なるtriplex塩基対を用いて検討しました。ターゲットDNA鎖と第三の鎖をDNAのフレームに組み込み、第三のDNA鎖の結合はワトソン - クリック塩基対を形成させることによって制御しました。三重らせん形成は、組み込まれたDNA鎖間の構造の変化を観察することによって検出しました。また、三重らせん形成は、光ケージした三本鎖を用いて検討し、第三のDNA鎖の光照射によるゲージの解除で、三重らせん形成を高速原子間力顕微鏡を用いて直接観察しました。設計したナノ空間を使って、第三のDNA鎖の結合を二本鎖DNAの形成および光ケージDNA鎖を用いることによって制御することができました。
3次元DNAオリガミ構造上に構築した光制御可能なプラズモニックナノシステム
Nature Communications, 7, 10591 (2016)
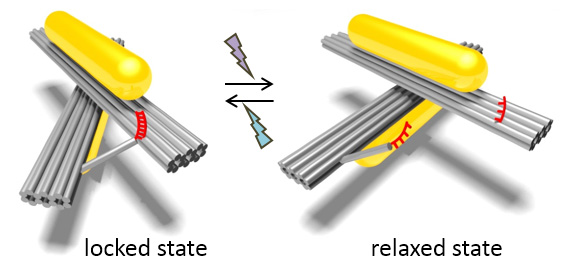
DNAナノ構造体上にすべて光によって制御可能なプラズモニックナノシステムを作成しました。このシステムでは、可動なDNAナノ構造体を使うことで光異性化分子のサブナノメートルの構造変化を増幅でき、DNAナノ構造体の立体異性に対応して、光異性化の分子運動を可逆なプラズモニック光学応答に変換することができます。プラズモニックナノ構造体は、中心を結合した2本の長方形からなるDNAオリガミ構造体に2個の金ナノロッドを結合して作成しました。光応答性部位は、光異性化分子修飾のDNA鎖からなり、これらをDNA構造体に導入しました。さらに、これらのプラズモニックナノ構造体のコンホメーション変化を光学にスペクトルとして読み出すことができます。私たちのシステムは、光照射によってDNAナノ構造のコンフォメーションを可逆的に「書き込み」と「消去」でき、異なるコンホメーションをプローブ光によって読み取ることができます。
光ピンセットを用いた1分子力測定によるDNAオリガミ構造中のHoliday Junction異性化の機械的性質の解析
Nucleic Acids Res. 44, 6574-6582 (2016)
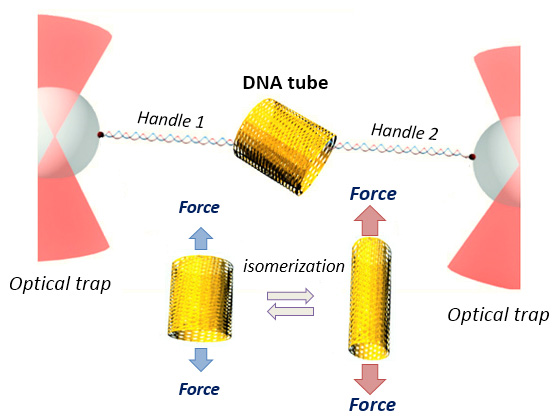
DNAオリガミ構造では、Holliday junctionを介して鋳型となる一本鎖DNAとステープルDNAが結合し、望みの形状を構築することができます。レーザートラップを用いて、個々のDNAオリガミ構造体の2方向の機械的特性を調べました。短いチューブと長いチューブの2つの構造に異性化可能なDNAチューブは、その機械的安定性(42-50 pN)について異方性を持っています。異なるDNAチューブと2次元DNAタイルを比較することで、機械的安定性は、特定の応力方向に沿ってHolliday junctionの密度によって決定されることが明らかとなりました。より低い力の範囲(26-30 pN)で、DNAチューブの形態変化の際に機械的な異性化が起こりますが、これは個々のHolliday junctionの異性化を足し合わせた挙動に起因しています。この結果から、Holliday junctionの異性化は、DNAオリガミ構造の機械的な挙動を制御するように使われることが示されました。ここで観察された機械的特性が優れたDNAナノ構造を設計するための指針となり、また、これらの機械的な異性化プロセスは、ナノセンサーやアクチュエータの開発のための新たな方法論となります。
光制御可能なDNA歩行分子の構築とDNAオリガミ上での分子運動の直接観察
Nano Lett. 15, 6672-6676 (2015)
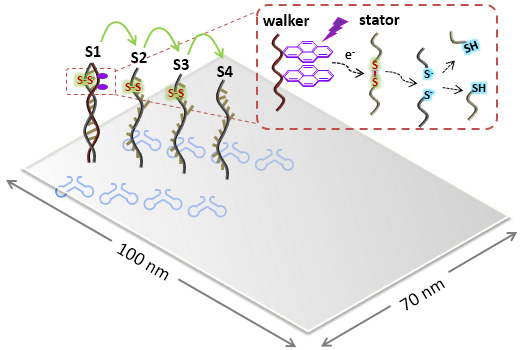
光で駆動する分子ナノマシーンDNA walkerの歩行をDNAナノ構造を使って検討しました。ピレンを導入したDNA walker鎖とジスルフィド結合を含む4本の1本鎖DNA鎖を2次元DNAタイル上にアセンブルしました。ピレンが350nmの光照射により励起することで、ジスルフィド結合の切断を誘導し、それによってDNA
walker鎖がDNAタイル上の1本鎖DNAに沿って最後の1本鎖に到達するまで連続的に移行します。DNA walkerの歩行する過程は、光照射時間によって、DNA walker鎖の位置をタイル上の1本鎖DNAの4つの位置で決め、その分布から求めました。また、DNA walkerの動きは、UV照射下で高速AFMを用いてリアルタイムで直接観察されました。この光駆動型ナノマシンは、メゾスコピック系における分子の輸送などの用途に使用可能です。
DNAナノ空間内でのグアニン四重鎖・i-motif形成部位での2本鎖DNAの形成と解離のの1分子操作
ACS Nano, 9, 9922-9929 (2015)
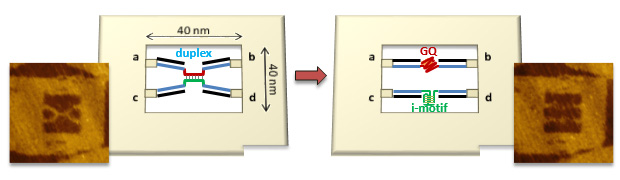
G四重鎖(GQ)と対応するi-motif配列を含む2本鎖DNAをDNAフレーム構造に導入し、一分子での操作と形成・解離の観察を行いました。 DNAフレームの中でのDNA鎖を連続的し操作し、トポロジー制御したGQ/i-motifの2本鎖NAを作成しました。 DNAフレーム内でのトーホールド鎖とK+の添加と除去によって、トポロジー制御したGQ/ i-motifの2本鎖DNAを高い収率で得ました。酸性条件でのK+の追加や操作により、2本鎖DNAは、1本鎖DNA、GQ、i-motifに解離しました。 GQとi-motifの形成される条件下での2本鎖DNAの解離は、高速原子間力顕微鏡(AFM)によって観察できました。以上のことから、DNAフレーム構造に制御され、2重鎖が巻き戻す方向に力がかかった状態では、GQ-とiモチーフ配列を含む2本鎖DNAを効率的に解離させることが示されました。
脂質二重膜上でのDNAオリガミの集合体の形成とその形成過程の1分子観察
Nature Communications, 6, 8052 (2015)
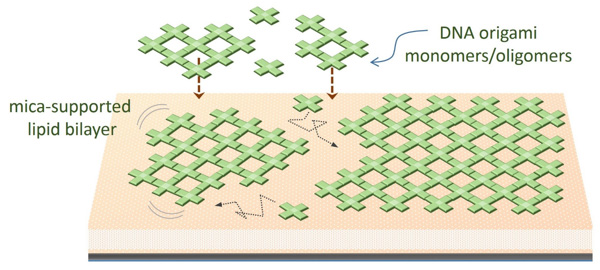
本研究では、2次元格子構造を形成するDNAオリガミ構造を組み立てるための脂質2重膜上での自己組織化の方法を開発しました。 マイカ上に脂質2重膜を作成し、この上にDNAオリガミ構造体を静電的に吸着しています。脂質膜に吸着された十字型のオリガミユニットが表面上を移動し、自己集合化することで、マイクロメートルサイズの大きな格子構造を形成することを見出しました。高速AFMによるイメージング技術を用いて、格子構造の成長と再構成などの様々な動的なプロセスを可視化しました。組み立てられた格子構造の表面修飾も可能で、ストレプトアビジンの結合する様子も観察できました。このアプローチは、ナノファブリケーションのための様々な構造体を構築するための新たな方法論であり、マイクロメーター空間でのナノデバイス作成への応用も可能です。
DNAナノ空間内でのZn2+依存性DNAザイムのDNA切断反応の1分子観察
Angew. Chem. Int. Ed. 54, 10550-10554 (2015)
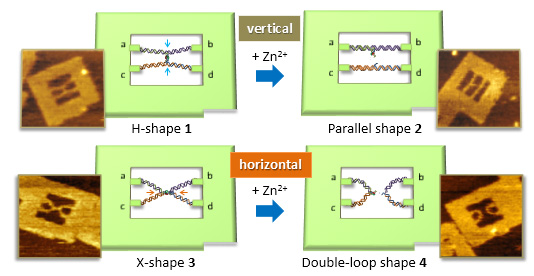
DNAオリガミナノ構造中でZn イオン依存性のDNAzymeの触媒反応の1分子イメージングを検討しました。 Znイオン依存性DNAzymeの1分子触媒活性は、設計されたナノ構造であるDNAフレームを使用して観察を行いました。DNAzymeと基質との2本鎖DNAを取り付けた2本鎖DNAを2つの異なるコンフォメーションでDNAフレームに組み込みました。反応の進行は、組み込まれた2本鎖DNAの構造の変化を観察することによりモニターし、DNAフレーム内でのDNA鎖の配置が反応後に明らかに変化したことが観察されました。高速AFMによってDNAzymeによる切断によって誘導される2本鎖DNAの解離を直接可視化しました。このイメージングシステムは、化学反応と生化学反応中の触媒反応を1分子観察するための実用的なツールです。
RNA-タンパク構造体を用いた細胞検出と機能制御
ACS Nano, 8, 8130–8140 (2014)
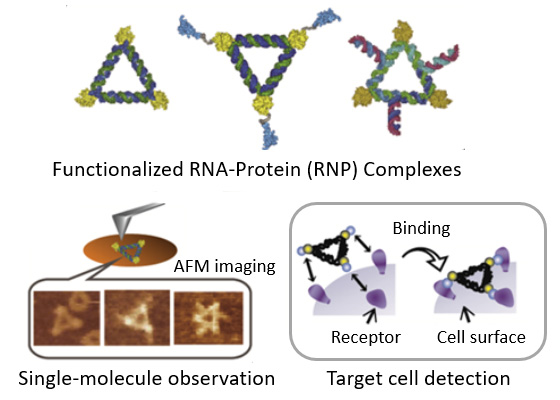
RNAタンパク質(RNP)複合体で構成される分子マシンは、分子ロボット、ナノメディシン、合成生物学の分野を拡大していくと期待されますが、機能的なRNPナノ構造を構築し、視覚化して、細胞機能を検出し、制御することは依然として大きな課題です。本研究では、モジュラー機能を備えたRNPナノ構造を設計し、RNPを1分子の解像度でリアルタイム可視化しました。RNP構造は高速AFMによって画像化し、RNP1分子の相互作用によって、ナノ構造形成をサポートするRNA足場の構造変化が誘導されました。特定のRNP相互作用により、血清含有バッファー中でのRNAナノ構造の安定性も改善されました。がん細胞またはノックダウン標的遺伝子を検出するため、タンパクまたはRNAモジュールを最適なサイズの同じRNA骨格に取り付けた機能性RNPを開発しました。このように、合成したRNPアーキテクチャは、ターゲット細胞を検出しその機能を制御できる新たなバイオマテリアルになると期待されます。
化学修飾したRNAオリガミ構造の構築
Chem. Eur. J. 20, 15330-15333 (2014)
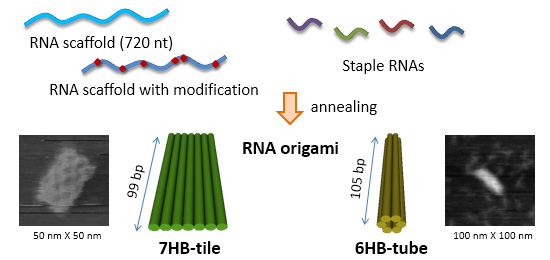
RNAはその構造と機能の多様性から注目されています。ここでは、構造の多様性を拡張するため、長鎖の1本鎖RNAとステープルとなるRNA鎖からRNAオリガミ構造体を設計しました。構造体は7本の2本鎖RNAからなるタイル構造体と6本の2本鎖RNA
からなるチューブ構造体を作成し、アニーング後に高率で構造体は形成されました。アミノ基やビオンチンを導入したRNA鎖からも構造体を作成でき、物性の異なるRNAオリガミ構造体の作成に成功しました。
光に応答して開閉可能なDNAナノカプセルの構築とナノ材料の捕捉と放出
Chem. Eur. J. 20, 14951-14954 (2014)
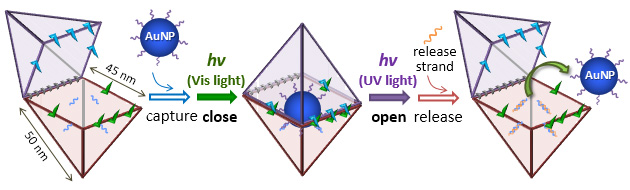
ナノ材料を運搬するため、2つの四角錐からなる光機能化したDNAナノカプセル(NC)を設計・構築しました。光制御可能な開閉システムとトーホールドを使い、光照射と鎖交換によってNCに金粒子を包摂・放出させる構造体を作成しました。NCの可逆的な開閉は電気泳動の移動度とAFMによって観察し、開く振る舞いは高速AFMによって直接観察しました。金粒子の包摂は金粒子に結合したDNA鎖とNC内部のDNA鎖の結合を使い、放出にはトーホールド配列を含むDNA鎖を使用しました。金粒子はNC内部に取り込まれ、NCを開いた後、鎖交換反応によって金粒子の放出に成功しました。外部応答性の薬物輸送と放出に応用可能です。
構造変化可能なDNAオリガミ構造体と光ピンセットを用いた力測定による1分子検出
Angew. Chem. Int. Ed. 53, 8137-8141 (2014)
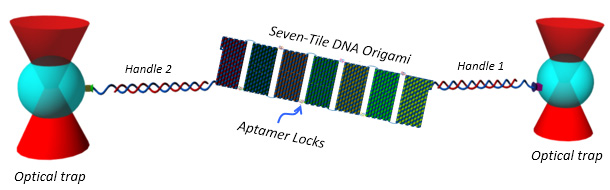
1分子の生体分子検出は検出限界として究極のものですが、1個の現象しか追えないのでその効率性から言うとよいものではありませんでした。この問題を解決するため、DNAオリガミ構造体を使ってメカノ化学的な方法で新たな検出システムを検討しました。6個の検出プローブを導入した、7枚のつながったDNAタイルを作成し、プローブにターゲット分子が結合するとタイルが開き、それを光ピンセットによって力と変位を実時間で検出します。この検出システムでは、10 pMの血小板由来成長因子(PDGF)を10分以内で検出でき、同時に検出できるターゲットDNA鎖と見分けることも可能です。この検出方法は今までできなかった高い効率での1分子のセンシングに使用できると期待しています。
らせん形成によるDNAチューブ構造体の構築とその性質
Angew. Chem. Int. Ed. 53, 7484-7490 (2014)
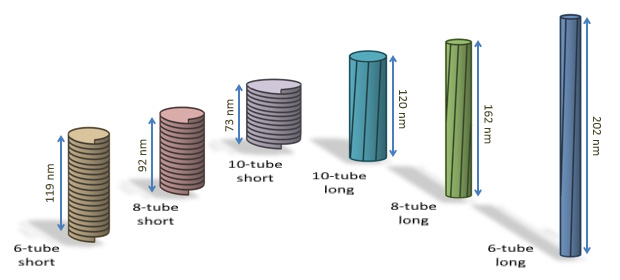
2本鎖DNAをテープ状に巻きつけることで、チューブ構造体を作成する新たな方法を開発しました。1周当たりの塩基対数を192, 256, 320とすることでチューブの直径と長さを設定できます。形成された構造体の表面をAFMで観察すると主に左巻きで、
1周当たりの塩基対数に応じて、長いチューブ構造体も形成されました。長いチューブは通常のチューブの2本鎖DNAの方向が組み変わった異性体であることもわかりました。特に1周192塩基対のもので長い構造体の形成が多くみられ、アニーリング条件で収率が変わることもわかりました。
脂質二重膜上での光応答性DNAオリガミ構造体の動的な集合と解離の1分子観察
J. Am. Chem. Soc. 136, 1714-1717 (2014)
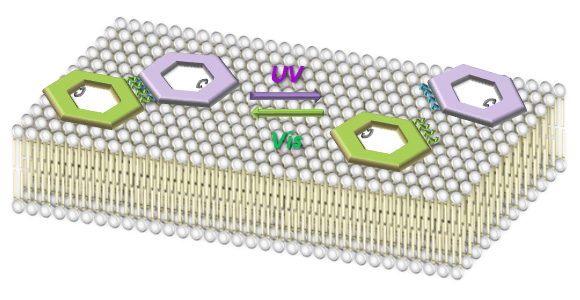
光応答性のDNAナノ構造体を作成し、その集合と解離を脂質2重膜表面で直接観察しました。光応答性DNA鎖導入した6角形構造体にコレステロールを導入し、脂質膜と相互作用によって観察系を構築しました。脂質膜上に置かれた6角形構造体は紫外光照射によって解離し、可視光照射によって再び集合し、その動的な挙動の観察を高速AFMによって行い、その観察に成功しました。
DNAナノ空間でのDNA組換え反応の直接観察とその人工的な操作
J. Am. Chem. Soc. 136, 211-218 (2014)
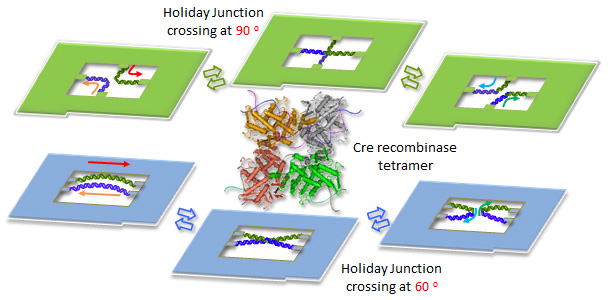
DNA組み換え酵素Creを用い、その組み換え反応を1分子観察で検討し、反応機構の解明と反応の制御を行いました。loxP配列の方向や距離、張力、角度を制御してDNAフレーム構造に導入し、高速AFMによって組み換え反応を1分子レベルで動的に検討ました。1対のloxP配列をDNAフレーム内に逆平行で固定してCreとの反応を検討すると、組み換え反応の進行が確認できました。次に、Cre四量体と基質DNAとの複合体を高速AFMによって観察すると、組み換え産物の生成とと4つのCreモノマーに分解する場面を捉えることにに成功しました。さらに、組み換え反応の方向性について、Holiday
Junction中間体に構造的なストレスをかけることで検討しました。その結果、Holiday Junctionが直交するものと60°で交差するものが、その組み換えの方向性について逆の挙動を示しました。このことから、DNAフレーム構造内に方向や角度を制御した2本鎖DNAを導入することで、DNAの高次構造が組み換えの方向性を決定することを明らかにしました。
DNAナノ空間でのHoliday Junction resolving酵素の反応の1分子解析
Nucleic Acids Res. 42, 7421-7428 (2014)
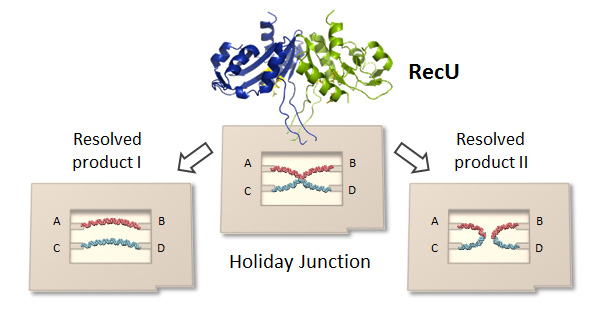
RecU resolvaseが基質であるHoliday Junctionをほどく反応を1分子観察しました。形成させたHoliday JunctionをDNA frameに導入し、RecUと反応させると、2つのほどかれた生成物が生成しました。Holiday Junction中心部の柔軟性に応じて反応の効率が変化することが分かりました。また、高速AFMによってHoliday Junctionから2つの生成物が生じる反応を実時間で1分子観察することに成功しました。
DNAフレーム構造内でのDNA制御配列上でのSox2-Pax6複合体形成の1分子可視化
Nano Lett. 14, 2286-2292 (2014)
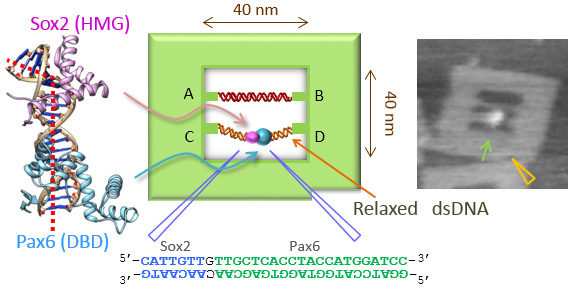
中枢神経系の発生の際に起こる、転写因子Sox2とPax6のDC5配列との複合体形成をAFMによって1分子観察しました。DNAフレームに異なるテンションをかけた基質となる2本鎖DNAを導入し、DNAを折り曲げて結合するSox2は、緩んだDNA鎖により良く結合することが確かめられました。また、Pax6はDNAに結合したSox2によって安定に複合体を形成することも明らかになりました。Sox2/Pax6のようにカップルした転写系では協調した複合体形成が行われることが示唆されました。
グアニンヘアピン二重鎖とグアニン三重鎖のDNAフレーム構造内での直接観察
Angew. Chem. Int. Ed. 53, 4107-4012 (2014)
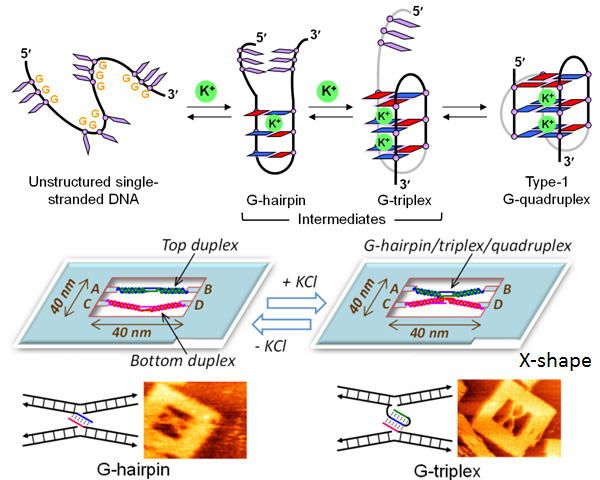
DNAフレーム構造を基質となるDNA鎖の構造を制御する手段として、新規なグアニン4重鎖逆平行構造と(3+1)グアニン4重鎖構造形成の中間体であるグアニン2重鎖と3重鎖構造をそれぞれ分子レベルの解像度で可視化しました。これらの中間体は安定かつよい収率で形成されました。実験結果をもとにグアニン4重鎖形成の過程を提案しました。
HIV‑1 Nucleocapsidタンパクの逆並行グアニン四重鎖形成のシャペロン効果
J. Am. Chem. Soc. 135, 18575−18585 (2013)
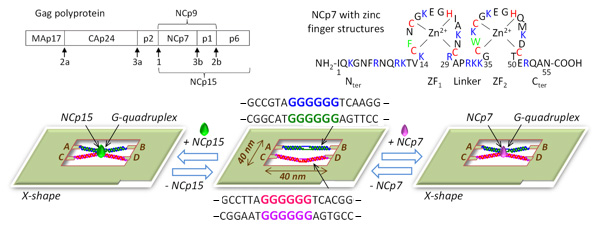
HIV-1 nucleocapsidタンパク(NCp)は核酸のシャペロンとして働き、グアニン4重鎖の形成に関与しています。DNAフレーム内に2本のグアニン2重鎖を導入し、NCp7とNCp15を加えるとどちらからもグアニン4重鎖となって結合し、シャペロンとして働くことが分かりました。これらの結合と脱離についても可視化することに成功しました。
DNAフレームを用いたグアニン四重鎖を形成するDNA鎖の方向の制御とその直接観察
Nucleic Acids Res. 41, 8738–8747 (2013)
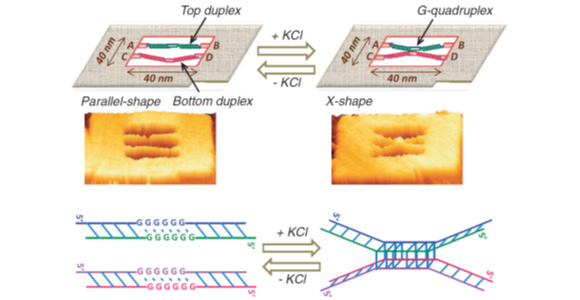
2本鎖DNA中に導入したグアニンの繰り返し配列をDNAフレーム構造に導入して、接合したグアニン4重鎖の形成を検討しました。KCl非存在下では導入した2本の2本鎖DNAは離れた状態ですが、 KCl存在下では中央で結合しX型を形成しました。4重鎖形成には2本鎖DNAの長さと、グアニンの数に依存することも分かりました。また、グアニン4重鎖構造の形成と解離を1分子で実時間観察できました。4本のグアニン繰り返し配列はその数や方向、当量をコントロールして導入できるため、溶液中ではできない構造を見ることも可能です。
DNAフレームを用いた2本鎖DNAの拘束によるB-Z転移の制御とZαβタンパクの結合の制御
Chem. Eur. J. 19, 16887-16890 (2013)
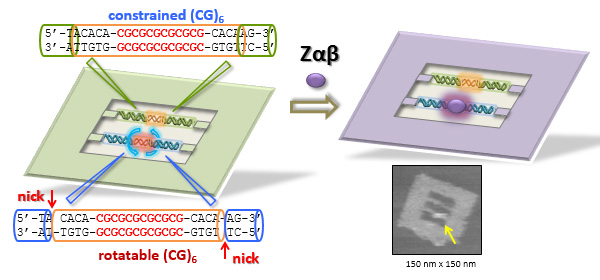
BZ転移では右巻きの2重鎖DNAが左巻きに回転することが必要です。Zαβ タンパクはZ型DNA構造をとるCG繰り返し配列に結合します。ここでは、CG配列を含む2本鎖DNAを使い、同じ配列でも一方は回転できない拘束されたもの、もう一方は切れ目を入れて回転できるようにしたものをDNAフレームに導入し、 Zab タンパクの結合の違いを検討しました。その結果、 Zab タンパクは回転できるCG配列の方に好んで結合し、拘束されたCG配列にはほとんど結合しないことが分かりました。このことは、2本鎖DNAの回転という物性によってタンパクの結合を制御できることを証明しています。
DNAナノ空間でのB-Z転移の直接観察
J. Am. Chem. Soc. 135, 1117-1123 (2013)
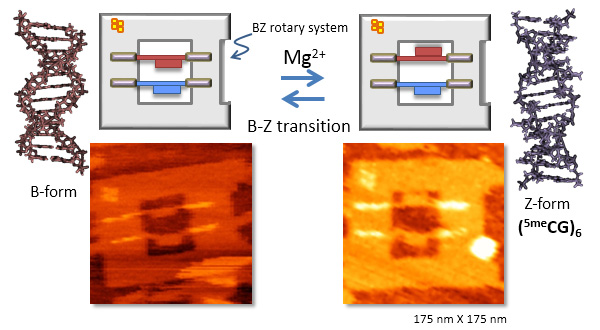
CG繰り返し配列の2本鎖DNAは塩濃度によって右巻きらせんのB型DNAから左巻きらせん構造であるZ型のDNA構造をとります。B-Z遷移を可視化するため、5-methyl-CG6回繰り返し配列を導入し、可視化のマーカーとなる3本の2本鎖DNAが並んだ旗となる構造体を結合し、DNA frame構造内に導入しました。これらの旗マーカーを持つ2本鎖は上側がBZ遷移を起こせるCG配列を含むもの、下側がコントロールとなる遷移しないランダムな配列を持つもので、それらの両側は回転を可能にするため、垂直方向に吊り上げたDNA frameを用いています。Mgイオンの濃度の上昇に伴ってマーカーとなる旗が下向きから上向きになる割合が上昇しました。また、Mgイオンの濃度を制御することで、B-Z遷移の平衡状態を作り、マーカーとなる旗が回転する様子を高速AFMによって直接観察することに成功しました。
DNAナノ空間での状態遷移を伴う2つの分子スイッチの挙動の直接観察
Chem. Commun. 50, 4211-4213 (2014)

2つの外部刺激(インプット)で2組の構造体の形成と解離を見るため、DNAフレーム構造内に3本の機能化した2本鎖DNAを導入しました。外部刺激には光とカリウムイオンを使い、2本鎖を形成・解離させる光応答性DNAとグアニン四重鎖を形成させるDNA配列を導入しました。K+非存在下で3本の2本鎖DNAを導入すると、光応答性DNAが2本鎖を形成し、
K+を添加し、UV光を照射すると、光応答性DNAの解離とグアニン四重鎖の形成が高速AFMによって1分子観察できました。逆に、 K+非存在下で可視光を照射するとグアニン四重鎖が解離し、光応答性DNAの2本鎖形成が観察されました。外部刺激とそれに依存した構造体形成によって1分子の論理ゲートを作成できます。
光応答性DNAオリガミ構造体の自己集合による様々な形状の構築
J. Am. Chem. Soc. 134, 20645-20653 (2012)
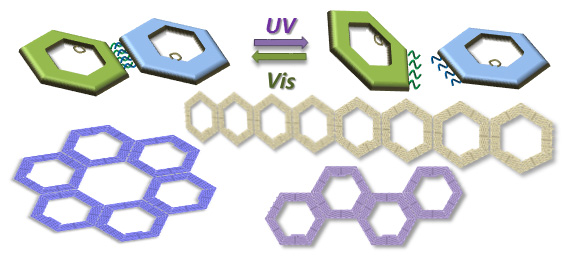
光応答性DNA鎖を6角形の構造体に導入し、それらを2次元の様々な方向にプログラム通りに配列できる新規な手法を開発しました。光照射によって可逆的にそれらの集合と解離を制御でき、6角形の構造体を直線的に集合させることができます。さらに、導入する光応答性DNAの数と位置をコントロールすることで、隣り合う構造体の裏表を制御でき、カーブした集合体構造や6個が集合した環状の集合体構造の構築に成功しました。
DNAナノ空間での光応答性2本鎖DNAの解離と結合の1分子可視化と可逆的なスイッチング挙動
Angew. Chem. Int. Ed. 51, 10518-10522 (2012)
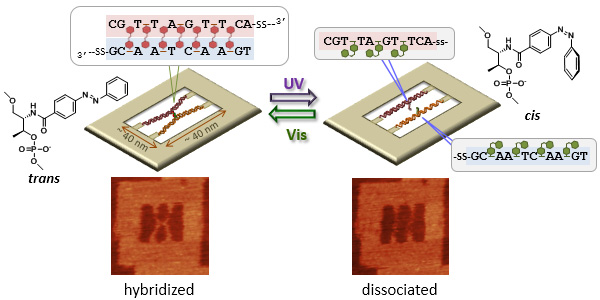
光応答性DNAを使った2本鎖DNAの形成と解離及びその機械的なスイッチングの動作を高速AFMを使って直接観察しました。アゾベンゼンを導入した光応答性DNA
(X. Liang, T. Mochizuki, H. Asanuma, Small, 2009, 5, 1761)を2本鎖に導入し、それらをDNA
frame構造内に結合しました。中央でコンタクトした2本の2本鎖DNAはUV光の照射によって解離し、この1分子観察システムでその動きを直接観察しました。さらに、可視光照射をすると、これらの解離した2本の2本鎖DNAは再び中央でコンタクトしました。このことから、DNA
frame内の2本の2本鎖の全体的な構造の変化を観察することで、光応答部位の解離と結合を可逆的なスイッチングとして1分子で可視化することに成功しました。
RNAを鋳型としたDNAナノ構造体の構築
Chem. Commun. 49, 2879-2881 (2013)

RNA転写物を鋳型として、設計したDNA配列とアニーリングすることで、RNA/DNAハイブリッドナノ構造体を構築しました。7本の2本鎖のバンドルした長方形構造と6本の2本鎖DNAがハンドル下チューブ構造の作成に成功しました。また、鋳型RNAにaminoallyl基やビオチン化した側鎖を導入した機能化RNA/DNAハイブリッドナノ構造体の構築にも成功しました。
DNAナノ構造上でのT7 RNAポリメラーゼの運動と転写の直接観察
Angew. Chem. Int. Ed. 51, 8778-8782 (2012)
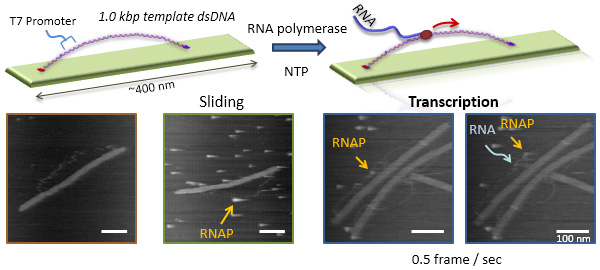
RNAポリメラーゼによる転写反応の全過程を高速AFMによる1分子観察で検討しました。この観察のため、400 nmのテープ状のDNAオリガミ構造体に、約1000塩基対の鋳型を2か所で導入した1分子観察用の構造体を作成しました。RNAポリメラーゼをDNA構造体に加え、高速AFMで観察すると、RNAポリメラーゼが鋳型DNA上をスライディングする様子が観察できました。転写反応では、鋳型DNA上をRNAポリメラーゼが1方向に動きながらRNAを合成する様子の観察に成功しました。
DNAナノ構造の機械的な操作による転写の制御系の構築
J. Am. Chem. Soc. 134, 2852-2855 (2012)
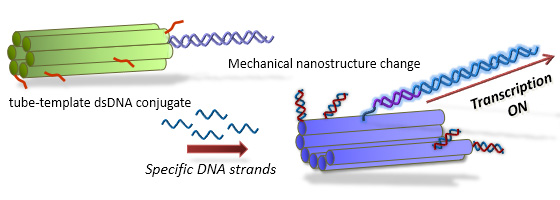
DNAナノ構造体の構造変換によって転写を開始できる系を作成しました。鋳型DNAのプロモーター領域に6本の2本鎖DNAからなるチューブ状のナノ構造体を結合し、チューブ構造の開環は、あらかじめ構造体に導入したDNA鎖に結合する特異的な1本鎖DNAによる鎖交換反応によって行いました。この結果、チューブ構造体を開くことができ、それに伴って、転写が抑制された状態から活性化された状態にできることに成功しました。
DNAナノ空間でのピロール・イミダゾールポリアミドの配列特異的なアルキル化
J. Am. Chem. Soc. 134, 4654-4660 (2012)
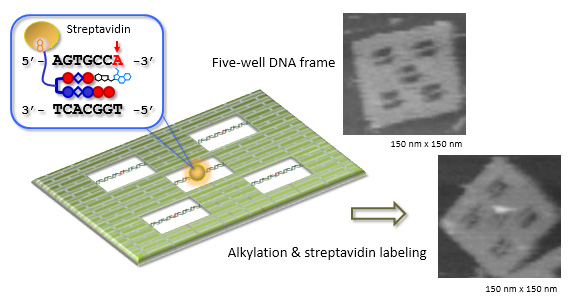
Pyrrole-imidazole polyamideのアルキル化の配列特異性を1分子で検出する手法を開発しました。ポリアミドにはアルキル化分子とビオチンを結合し、特異的な配列のアルキル化後、ストレプトアビジンによるラべリングで可視化しました。5つの空間を持つDNAオリガミ構造体にそれぞれ5つの異なる配列の2本鎖DNAを導入し、1塩基のミスマッチとアルキル化できる塩基がない状態での結合性の違いを検討しました。その結果、アルキル化によって正確な配列に88%の特異性で結合し、1分子でもポリアミドが1塩基のミスマッチを読み分けていることがわかりました。
DNAオリガミ上の経路のネットワークを歩行するDNAモーター
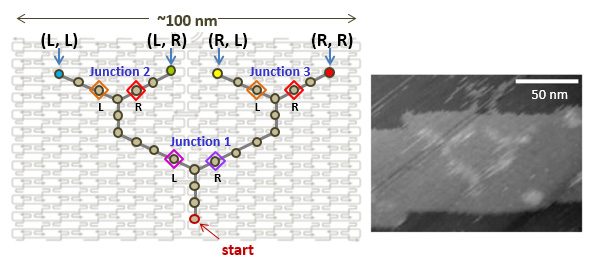
Nature Nanotechnology, 7, 169-173 (2012)
複数に分岐した複雑な経路をDNAオリガミ上に作成し、指令に従って、DNAモーターの進行方向をナノスケールで制御できる手法を開発しました。DNAオリガミ構造体の上に、1本鎖のDNAを等間隔に並べ、3つの分岐点がある経路を作成し、それらの左右両側にゲートを設け、進行方向を制御しました。DNAモーターはあらかじめゲートの閉じていない方向へ進行し、指令に従って4つの最終地点へ誘導でき、この動きをAFMによって1分子で捉えることに成功しました。
DNAモーターの運動の直接可視化
Nature Nanotechnology, 6, 166-169 (2011)

本研究ではDNAを用いた移動可能な分子機械(DNAモーター)をDNAナノ構造体上で制御して動かし、その運動を高速AFMによって可視化しました。DNAモーターは1本鎖DNAが制限酵素の切断により、近接する相補鎖に移動する分岐移動の原理を用いています。17本の1本鎖DNAをDNAナノ構造上に導入したトラック(経路)を作成し、その末端に移動するDNAモーターを導入しました。ニッキング酵素を加えると、順次隣接するDNA鎖に移動し、トラック上を経時的に1方向に動くことが明らかとなりました。次に、DNAモーターがトラック上を移動する様子を高速AFMによって観察しました。DNAモーターはAFMの走査時間内で移動するところが直接観察でき、その運動解析するとDNAモーターがトラック上の1本鎖DNAを順次移動することが明らかとなりました。
DNAナノ空間でのグアニン四重鎖形成と解離の動的な1分子観察
J. Am. Chem. Soc. 132, 16311–16313 (2010)
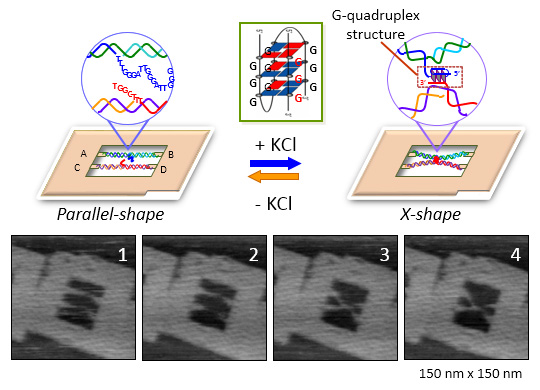
グアニン4重鎖は生体中で遺伝子の制御に重要な役割をしています。DNAの動的な構造変化を1分子レベルで実時間観察できる系の構築を目指し、グアニン4重鎖構造の形成で誘導されるナノスケールの構造変化を検出する系を構築しました。分割した[3+1]グアニン4重鎖の配列を2本の2本鎖DNAそれぞれの中心に導入し、DNAフレーム構造内に固定しました。DNAが並んだDNAナノ構造体にK+を添加すると2本鎖DNAが中心で結合したX型のナノ構造が観察されました。次に、グアニン4重鎖構造の形成を高速AFMによって実時間で観察しました。K+を含む観察用の溶液中AFMを走査すると、走査中にX型構造を形成するものが観察されました。以上のように、DNAナノ構造体を用いて、2本鎖DNAの構造変化からグアニン4重鎖の形成を動的に1分子で観察する系の構築に成功しました。
DNA修復酵素の直接解析のためのDNAナノチップの開発
Angew. Chem. Int. Ed. 49, 9412–9416 (2010)
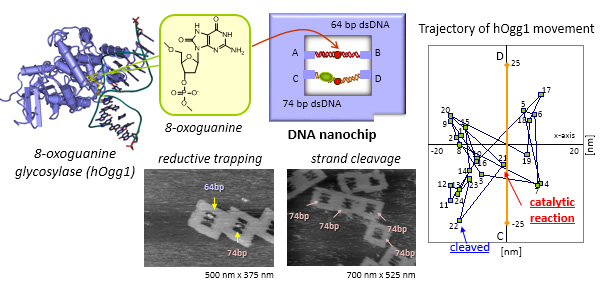
DNAフレームの1分子観察系を使用しDNA修復酵素(8-oxoguanine glycosylase, pyrimidine dimer glycosylase)の1分子観察と反応の制御を行いました。これらの酵素はDNA鎖を折り曲げることで修復反応を行うため、64塩基対と緩んだ状態の74塩基対の2本鎖DNAをDNAフレーム内に導入し、反応の制御と修復酵素の反応の挙動を解析しました。還元による酵素の捕捉と切断反応の反応効率を解析した結果、74塩基対の配列がより反応しやすく、ナノ構造体によって酵素反応を制御できることが示されました。また、高速AFMによって、酵素1分子の挙動が可視化でき、DNAへの結合、DNA上での運動、触媒反応、DNAからの解離といった一連の酵素反応の1分子観察が可能となりました。
DNAナノ空間での異なる張力の2本鎖DNAによるDNAメチル化酵素の制御と直接観察
J. Am. Chem. Soc. 132, 1592–1597 (2010)
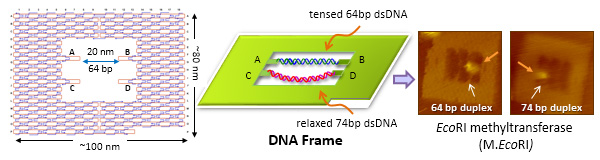
生体分子の1分子の運動の可視化は、分子の挙動やその反応を解析でき、分子の持つ固有の振る舞いを見ることが可能となります。本研究では、基質となる2本鎖DNAを導入できる2次元DNAナノ構造体「DNAフレーム」構造を設計し、その中に2本鎖DNAを導入し、酵素反応の1分子観察を行いました。メチル基転移酵素(M. EcoRI)はDNA鎖を折り曲げることでメチル化反応を行うため、張った状態の64塩基対と緩んだ状態の74塩基対を導入し、M.EcoRIのDNA鎖への結合の挙動を高速AFMによって解析しました。メチル化反応効率をAFMによる1分子観察と生化学的手法で解析した結果、74塩基対の配列がよりメチル化されやすいことが明らかとなりました。このことから、DNAフレーム構造によって2本鎖DNAの構造を変えることで酵素反応を制御できることが示され、酵素の挙動の1分子解析も可能となりました。
光架橋反応を利用したDNAオリガミ構造体の高温での安定化
J. Am. Chem. Soc. 133, 14488-14491 (2011)
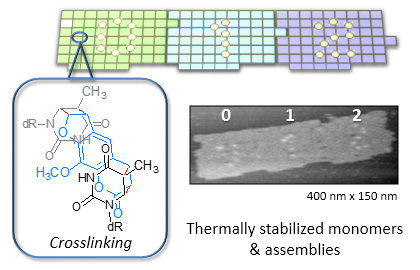
DNAオリガミ構造の熱に対する安定性を向上させるため、8-methoxypsoralenの光架橋反応を利用しました。光架橋によってモノマーの安定性は解離温度で30℃程度向上し、80 ℃のような高温でも形状を維持できることを確かめました。この光架橋したモノマー3種類を使って、高温から自己集合させると、集合体はデザイン通り自己集合し、その収率も向上しました。このことから光架橋は結合部位の1本鎖には作用しにくいこともわかりました。
DNAジグソーピースを使ったプログラムした2次元自己集合
ACS Nano, 5, 665-671 (2011)
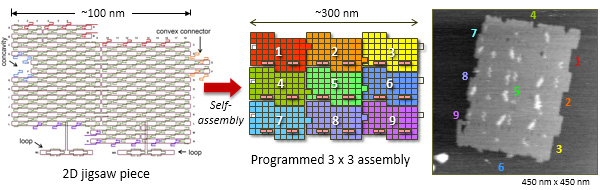
2次元に拡張可能なDNAジグソーピースを使ってプログラム可能な集合系の設計と構築を検討しました。2次元ジグソーピースは塩基配列の相補性、形状の相補性、π相互作用を組み合わせ、1次元方向(2重らせん軸方向)と2次元方向(2重らせん軸に直交方向)に配列できるように設計しました。9種類の異なる2次元構造体ユニットを設計し、自己集合させました。その結果、塩基配列のプログラムどおりに異なるユニットが1次元方向と2次元方向に配列され、目的とする3 x 3集合体を構築することに成功しました。また、9個のジグソーピース上に文字を導入し、自己集合後DNA JIG SAWと表示することに成功しました。
4方向に結合するDNA構造体を使った2次元自己集合
Chem. Commun. 47, 3213-3215 (2011)
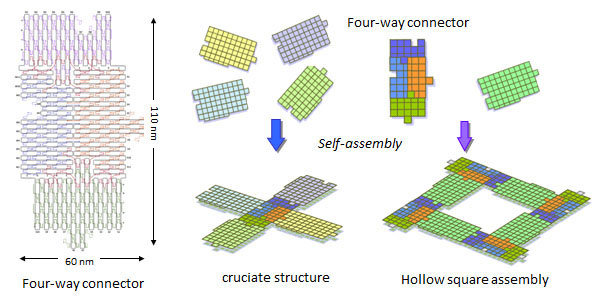
2次元集合体の多様性を増やすため、中心となる新規なDNAオリガミ構造体を設計し構築しました。この4方向コネクター構造体では、π相互作用を4方向で行うため、4方向に2重らせん軸を向ける設計を行い、他のジグソーピースモノマーと安定に結合できるようにしています。この4方向型コネクターと4個の異なるDNAジグソーピースを用いることで、自己集合によって十字型集合体の構築に成功しました。さらに、4方向型コネクターと1種類のDNAジグソーピースから中空な四角形(口の字型)構造を構築することに成功しました。
DNAジグソーピースを使ったプログラムした自己集合系の構築
Chem. Eur. J. 16, 5362–5368 (2010)
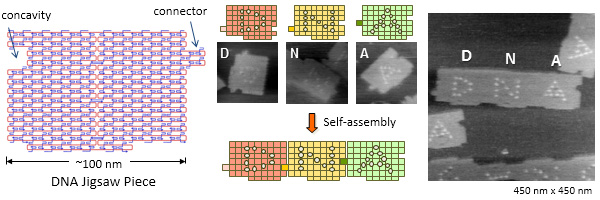
2次元DNA構造体をDNA塩基配列のプログラムで配列する系の構築を検討しました。「DNAジグソーピース」と名付けた2次元ナノ構造体にDNA塩基配列、形によるフィット、π相互作用を組み合わせ、1次元に配列できるように設計しました。さらに、複数種類のオリガミを正確に並べるために、凸凹の位置を変え、横方向にフィットして並ぶように5種類の異なるオリガミを設計しました。この系ではまず、一段階目の自己集合で個々のオリガミを作成し、次に二段階目の組織化でそれらを並べる、二段階の自己集合の方式を採用しました。識別のためのヘアピン型のDNAマーカーを用い、ジグソーピース表面上にドットでアルファベットを表示したものを作成しました。ジグソーピースに順番にD,N,Aの文字を導入し、3個のオリガミで自己集合させるとDNAの文字が表示できました。また、4個及び5個のジグソーピースから自己集合させるとNANOとKYOTOの単語をそれぞれ表示できます。
複数の長方形の折りたたみによる錘状構造体の構築
J. Am. Chem. Soc. 131, 15570–15571 (2009)
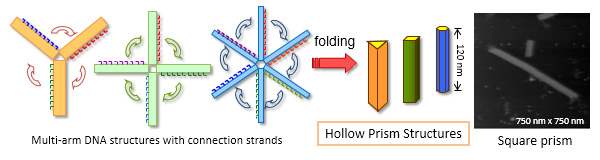
2次元DNAナノ構造から組み上げる新規な3次元構造体の設計と構築法の検討を行っています。3個、4個、6個の長方形構造を持つ2次元DNAナノ構造を設計し、これらの長方形構造間を結合するコネクションDNA鎖を導入し自己集合させると、中空な柱状構造(プリズム構造)が形成されました。さらに高速AFMによってスキャンを続けることで、形成されたプリズム構造を開環することができ、その動的な形態変化を1分子で詳細に解析できました。
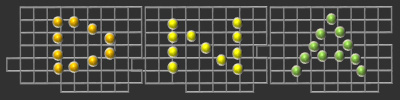
DNAオリガミとは?
DNAの自己集合によって作成されるナノスケールの2次元構造体。2006年にカリフォルニア工科大学のRothemundによって開発された。(a)鋳型となる長い1本鎖DNA(約7千塩基)に短い相補鎖DNAを加え、加熱し、ゆっくり冷却することで、あらかじめ設計したDNAナノ構造体と同じ形にDNAを分子集合させることができる。相補鎖DNAに分子を結合すれば、思い通りの位置に分子を導入できる。(b)本グループで設計したDNAナノ構造体と形成された構造体のAFM画像。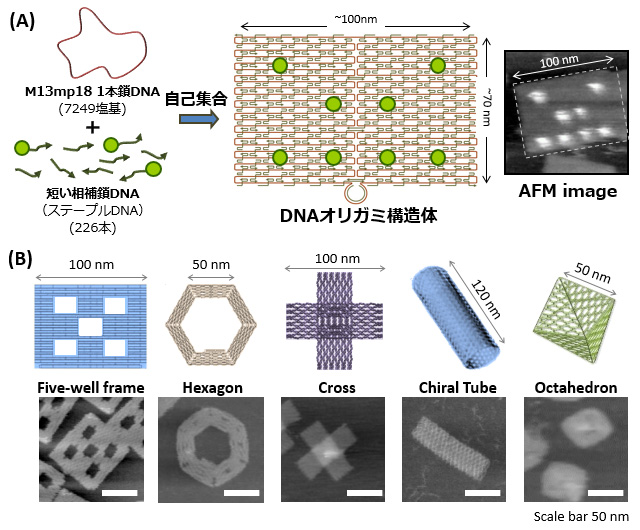
バナースペース
DNAナノテクノロジーグループ
京都大学大学院理学研究科
物質―細胞統合システム拠点
〒606-8501
京都市左京区吉田牛ノ宮町